央广网上海12月16日消息(采访人员杨静 通讯员潘少军 贾龙豪)复旦大学类脑研究院青年研究员路易斯·佩德罗·科埃略(Luis Pedro Coelho)、教授赵兴明、名誉教授皮尔·伯克(Peer Bork)与来自德国、西班牙、美国、英国等多国科学家合作研究 , 基于全球微生物组(global microbiome)的概念 , 将地球上不同栖息地的微生物作为统一系统 , 运用人工智能技术对1.3万个公开宏基因组样本进行挖掘 , 构建了迄今为止最全面的全球微生物基因目录(GMGC, Global Microbial Gene Catalog) , 为全球微生物组研究迈出了重要一步 。 该研究同时发现 , 大多数基因具有栖息地特异性 , 跨越多栖息地的基因主要富集在抗生素耐药性基因和移动遗传元件 。
北京时间2021年12月16日凌晨 , 相关研究成果《原核生物基因的生物地理学研究》(“Towards the biogeography of prokaryotic genes”)以长文(Article)形式发表于《自然》(Nature)主刊 。 科埃略是论文的第一作者和共同通讯作者 。 该研究得到了欧盟“地平线2020”创新计划、国家重点研发计划、国家自然科学基金、上海市“脑与类脑智能基础转化应用研究”市级科技重大专项等项目的资助 。
构建迄今为止最全面的全球微生物基因目录
基因目录对于描述微生物群落的物种组成和功能特性具有重要意义 。 自2010年欧洲分子生物学实验室(EMBL)和华大基因构建首个人类肠道微生物基因目录以来 , 新兴的微生物基因目录为研究人类生理学和疾病提供了重要线索 。
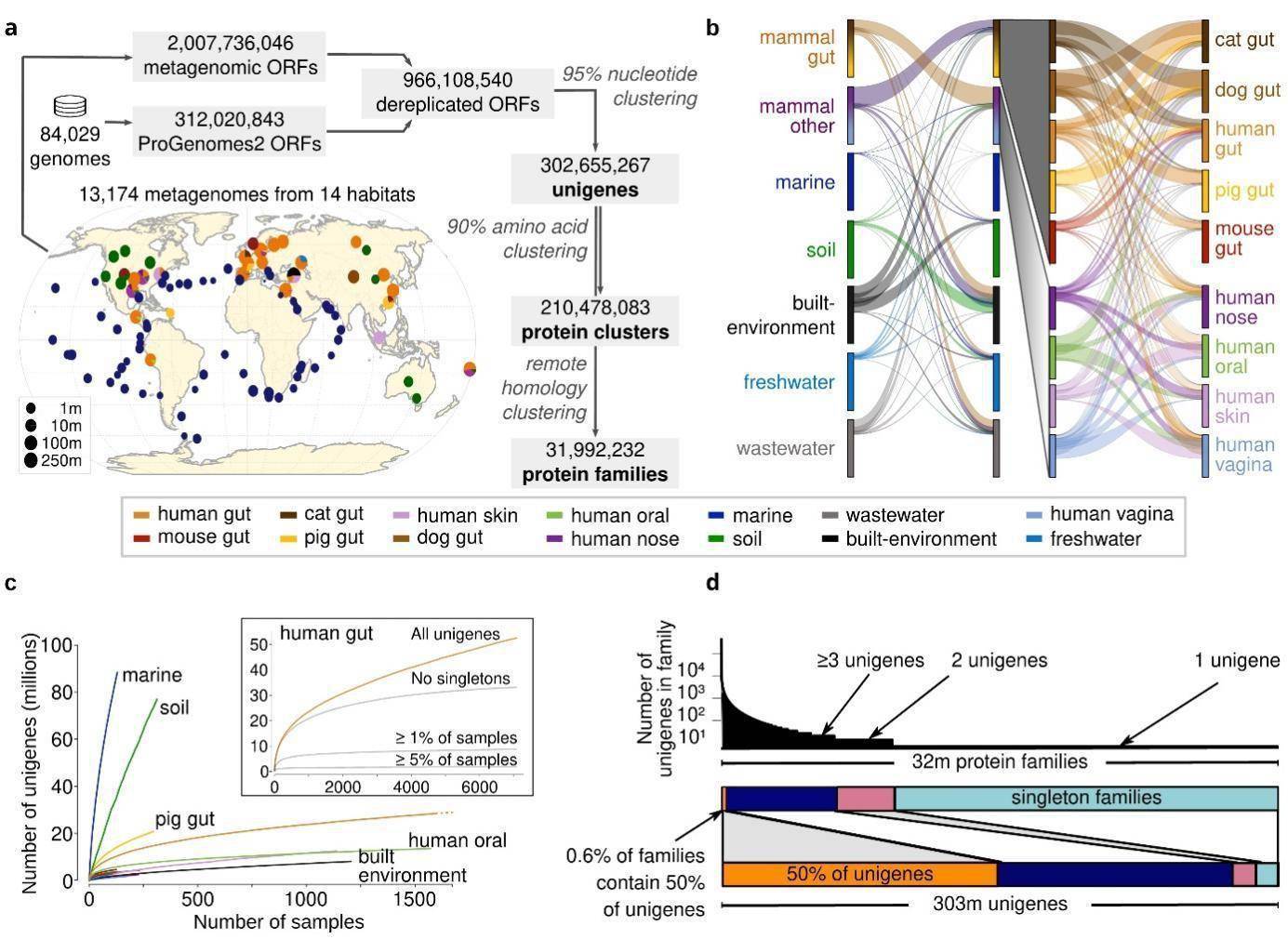
全球微生物基因目录涵盖了肠道、口腔、皮肤、海洋、土壤等14微生物的主要栖息地 , 收集了13174个公开可用的高质量宏基因组和84029个高质量的基因组 , 得到了包含3.03亿个物种级的基因(95%的核酸一致性聚类) , 构建了迄今为止最全面的全球微生物基因目录 , 将为地球生态研究和人类健康研究提供重要贡献 。
文章图片
从1.3万个宏基因组样本和近10万个细菌基因组中构建的包含3亿个原核生物基因的全球微生物基因目录
揭示微生物基因与栖息环境的重要关联
物种水平的单基因簇(unigene)可能代表着来自多种栖息地的基因(multi-habitat genes) 。 多栖息地基因可能来自在多种栖息环境中都生存的物种 , 或者来自基因组之间或者跨越栖息地边界水平转移的移动遗传原件(mobile elements) 。 研究发现 , 大多数基因都是栖息环境特异性的 , 这与微生物倾向于适应环境的特性是一致的;只有5.8%物种水平的单基因簇是多栖息环境基因 , 多栖息环境基因主要富集在抗生素耐药性基因和移动遗传原件 。
推荐阅读
- 测试|图森未来完成全球首次无人驾驶重卡在公开道路的全无人化测试
- ASUS|华硕预热ROG Flow Z13:称其是“全球最强悍的游戏平板”
- IT|全球汽车行业价值两年突增至3万亿美元 中国电动车企立大功
- IT|全球供应25亿剂疫苗 科兴上半年营收110亿美元
- IT|全球每日新增确诊病例首超100万例 世卫:两大毒株正掀起“疫情海啸”
- Tesla|特斯拉在美国召回约47.5万辆汽车 接近其去年全球交付总量
- 堆芯|全球首座,世界领跑!
- 集聚|向全球应用创新策源地持续迈进 上海“双千兆”应用体验中心正式揭牌
- 核心|中科大陈秀雄团队成功证明凯勒几何两大核心猜想,研究登上《美国数学会杂志》
- 疫苗|中国生物:全球首支获批使用二代新冠疫苗将在阿联酋用于序贯接种